SeqCP -環狀序列重組蛋白質搜尋方法
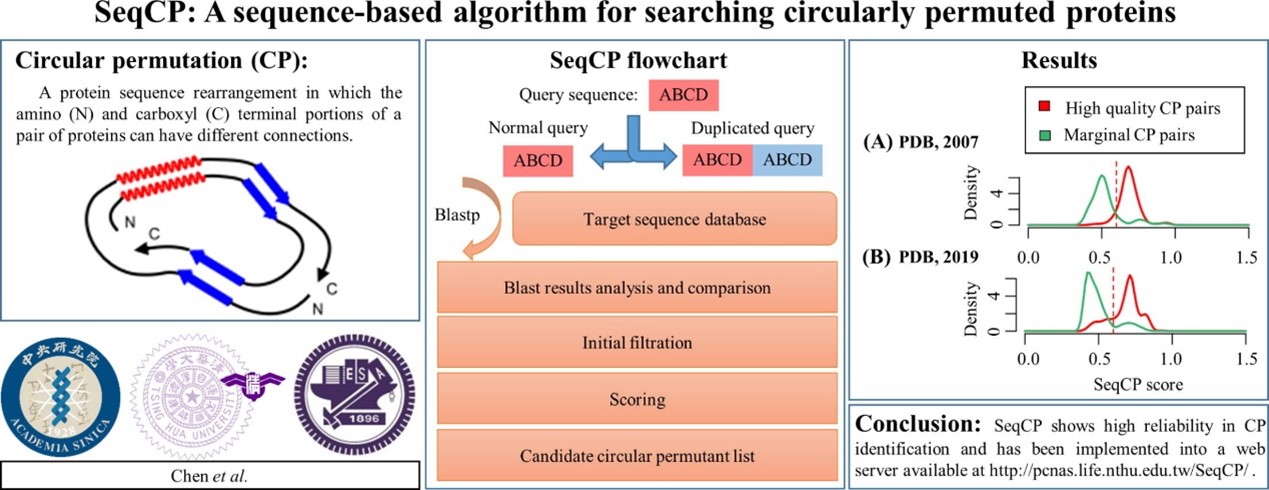
蛋白質環形結構重組技術(Circular Permutation, CP)是一種在蛋白質結構、蛋白質功能和生物工程技術等領域應用的方法。目前,大多數CP檢測算法都需要蛋白質結構訊息進行分析,但由於許多蛋白質的結構尚未被解析,因此很多CP組合無法被識別。為了解決這個問題,本核心呂平江教授研究團隊開發了一種基於蛋白質序列的高效率CP檢測器,可以識別更多的CP組合,並促進蛋白質研究的進展。SeqCP的網址是:http://pcnas.life.nthu.edu.tw/SeqCP/
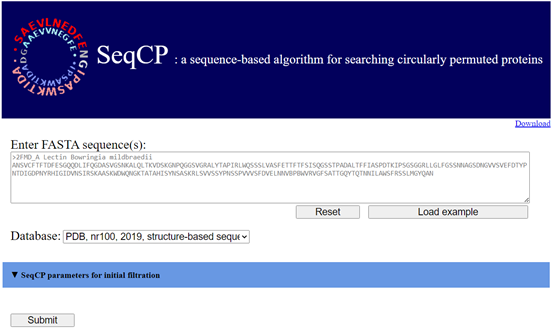
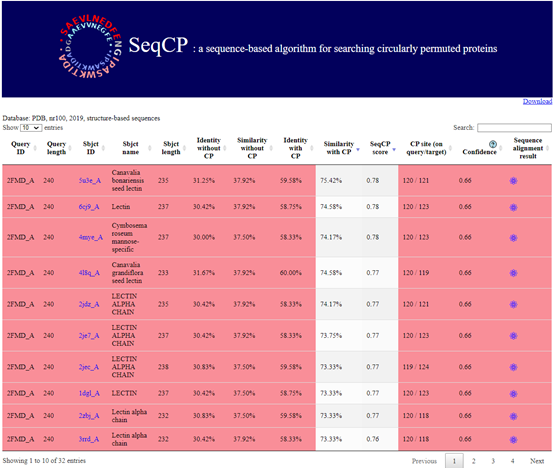
SeqCP提供了一個簡潔易懂的使用介面,使用者只需將序列直接貼上並提交,即可獲得搜尋結果。此外,SeqCP也提供使用者自訂參數,可以做進一步的篩選。
SeqCP是近年來第一個能依據蛋白質序列有效辨識環狀序列重組蛋白質的搜尋系統,SeqCP的優勢在於:
- 使用者只需提供蛋白質序列資訊進行分析。
- SeqCP高效且易於使用。使用者可通過網站操作,亦可自行下載程式使用。
- 速度比當代使用蛋白質結構搜尋環狀序列重組蛋白質的方法快33倍,有利於進行大規模搜索。
- 能整合進其他演算法及協助不同研究領域應用。
使用SeqCP搜尋系統,可以利用蛋白質序列來辨識環狀序列重組蛋白質,這個系統能夠高效率地識別CP組合,從而增加了蛋白質研究的廣泛應用。通過這項研究,我們希望能夠推動CP技術的發展,並為蛋白質研究提供更多有價值的資源和工具。
參考文獻:
Chen CC, Huang YW, Huang HC, Lo WC, Lyu CP. (2023) SeqCP: A sequence-based algorithm for searching circularly permuted proteins. Comput Struct Biotechnol J. 21:185-201.